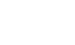成果简介
近日,澳大利亚昆士兰大学水管理高等研究中心(AWMC, The University of Queensland)和华大在Environmental Science & Technology Letters上发表题为“Novel Multiplexed Amplicon-Based Sequencing to Quantify SARS-CoV-2 RNA from Wastewater”的研究论文。文章介绍了一种基于多重扩增子的测序方法(Multiplexed Amplicon-based Sequencing)来实现城市污水中SARS-CoV-2 RNA的精确检测。值得一提的是,该研究采用了华大智造全面、灵活且高效的MGISEQ-2000基因测序仪,以及ATOPlex多重PCR定制化平台来完成。
和常规的RT-qPCR相比,该方法不仅能够对新冠病毒进行高灵敏度检测,还能准确获取病毒载量信息和病毒基因组信息,利用这些信息可以对城市疫情流行程度进行判断并对大流行的新冠病毒变种进行溯源。此外,研究结果表明城市污水中的固相悬浮物或颗粒物中亦含有大量的SARS-CoV-2 RNA。该研究有望进一步推进基于污水流行病学在公共卫生应急方面的应用。
引言
当前由于SARS-CoV-2引起的新冠肺炎全球大流行是国际社会广受关注的突发公共卫生事件。截止到7月12日,全球范围内已经有超过1.8亿人感染,并造成了超过四百万死亡病例。非药物性的干预,包括社交距离、佩戴口罩、及时隔离感染者和密切接触者、以及限制人类活动范围,被各国政府所采纳以减缓新冠病毒社区传播。
然而,因为不少的病毒携带者属于无症状患者,通过临床验测来衡量社区内病毒的流行程度有一定的局限性和滞后性。最新的研究进展表明,基于污水的流行病学研究(Wastewater-Based Epidemiology, WBE)可在早于医疗系统检测的时间点发现病毒的存在,同时不受无症状感染者的干扰,这为新冠疫情的管控从另一层面提供了新的预警信息,并能帮助相关部门更加有效地做出公共卫生决策。
随着COVID-19的大流行,WBE日益受到各国政府卫生机构和研究团队的关注。但是由于SARS-CoV-2在污水中的浓度很低,如何准确、灵敏和高通量检测城市污水中的SARS-CoV-2依然面临挑战。
目前的检测方法主要有哪些呢?
目前常规检测方案多数基于聚合酶链反应(PCR),如反转录实时荧光PCR (RT-qPCR)和以及反转录微滴数字PCR (RT-ddPCR)。RT-qPCR和RT-ddPCR虽然很灵敏,但由于城市污水管网是一个庞大而且复杂的体系,RNA在污水中会被高度稀释和降解。另一方面,RNA病毒极不稳定,从而从环境中得到高质量的基因组相当困难。RT-qPCR和RT-ddPCR一般使用的N1/N2/N3扩增引物,相对于病毒基因组(~30000bp)覆盖区域低于1%。这意味着假如引物靶位RNA序列被降解,会造成假阴性结果(脱靶)。
你也许会想宏转录组(Metatranscriptomics)检测手段是否可行?与基于PCR的方法相比,宏转录组技术的优势在于它可以捕获到环境中的所有RNA病毒片段,从中可以得到SARS-CoV-2的基因序列。可是,由于病毒颗粒在离开人体进入城市污水管网之后会被高度稀释和降解,降解的病毒片段会和其他污水微生物(sewagemicrobiome)参杂在一起。所以要想采用宏转录组定量污水中SARS-CoV-2,需要对城市污水样本完成超深度的测序(ultra-deepsequencing),这意味着大量资金投入,并需要后续搭配高度专业化的生物信息分析流程。
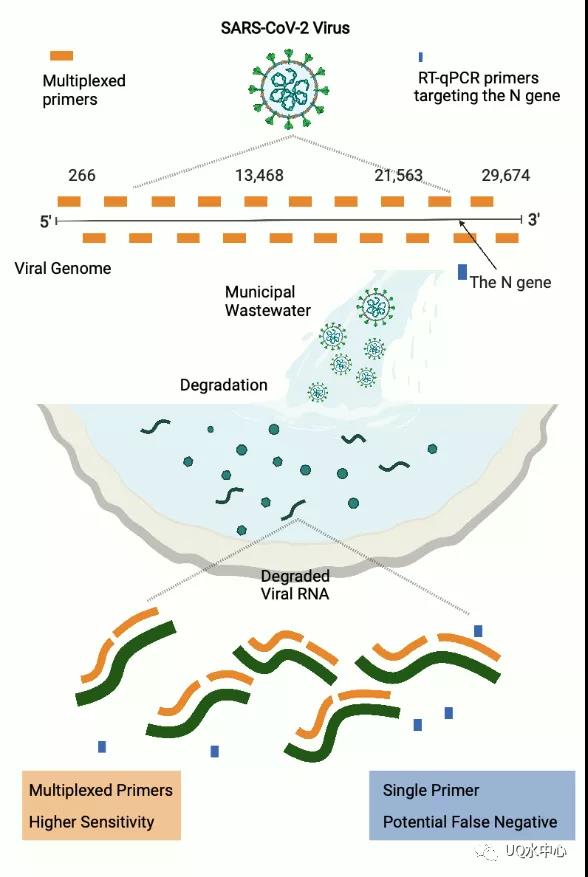
可以看出,一个成本低、效率高的测序方法显得很有必要。多重 PCR测序技术(MultiplexedAmplicon-based Sequencing)是在常规 PCR基础上发展出来的一种新型测序技术,能够同时对多个靶位进行检测,不仅节省了时间和成本,更能从有限的基因组中提取大量的信息。ATOPlex是华大智造(MGI)开发的多重PCR技术平台,通过使用多重混合引物捕获新冠病毒全基因组序列信息,可实现对低浓度病毒的富集和高通量测序。这个新的测序方法操作流程简单(见图1),既有极高的灵敏度,又能够精准定量病毒,还能获取完整的基因组信息,从而实现病毒检测、定量和溯源分析。
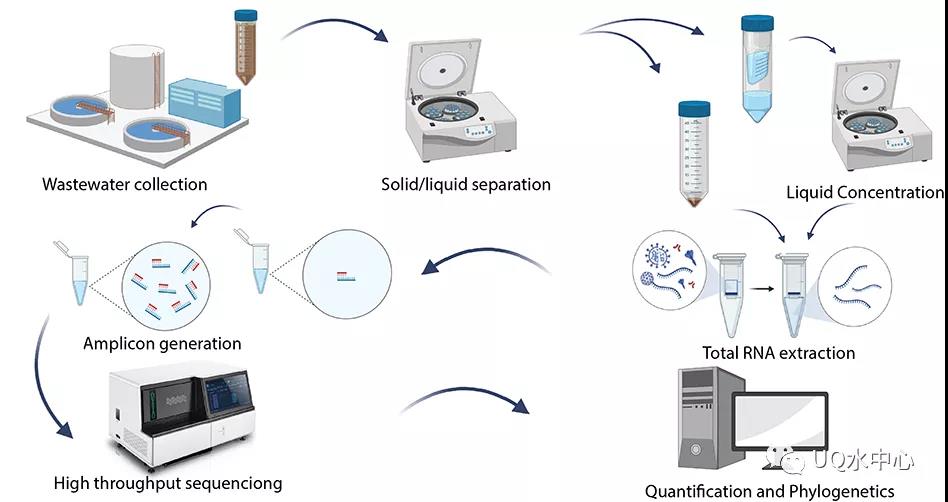
图1. 城市污水新冠病毒检测流
结果与讨论
ATOPlex可实现更灵敏的病毒定量
同时对梯度稀释的阳性样品进行RT-ddPCR绝对定量和ATOPlex测序,ATOPlex获得的新冠reads数量比例(SARS-CoV-2/Spike-incontrol)与病毒浓度成高度正相关(R2 = 0.993),病毒序列的比例可以很好的代表病毒含量。
图2.ATOPlex和RT-ddPCR相关性分析
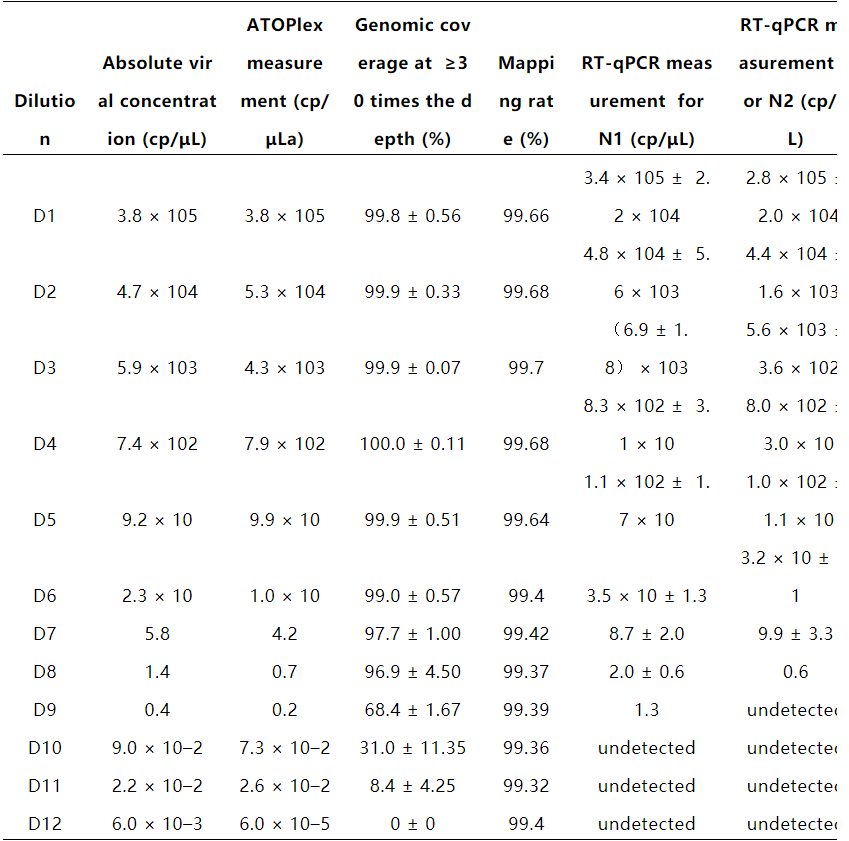
此外,通过比较发现,ATOPlex技术比常规的RT-qPCR更加灵敏。当病毒含量在RT-qPCR检测限附近,RT-qPCR可能会给出假阴性,但ATOPlex可以稳定地获取病毒基信息,并且能够获取96.9%的基因组信息,甚至在病毒浓度低于检测限一个数量级时,ATOPlex仍然可以回收到8.4%的病毒基因组(见表1)。所以ATOPlex技术可以更灵敏地检测污水中低浓度的病毒。
表1. ATOPlex和qPCR对N1和N2引物检测的标准偏差比较(阳性对照品稀释系列)
ATOPlex可实现病毒溯源分析
RT-qPCR只能给出定量信息,然而ATOPlex测序技术能够尽可能的恢复病毒的基因组信息,从而准确、快速的对病毒变种进行溯源。针对阳性样品基因组的系统进化学研究分析发现,在病毒浓度低于RT-qPCR检测极限四分之一的条件下,溯源的结果依然准确(图3)。
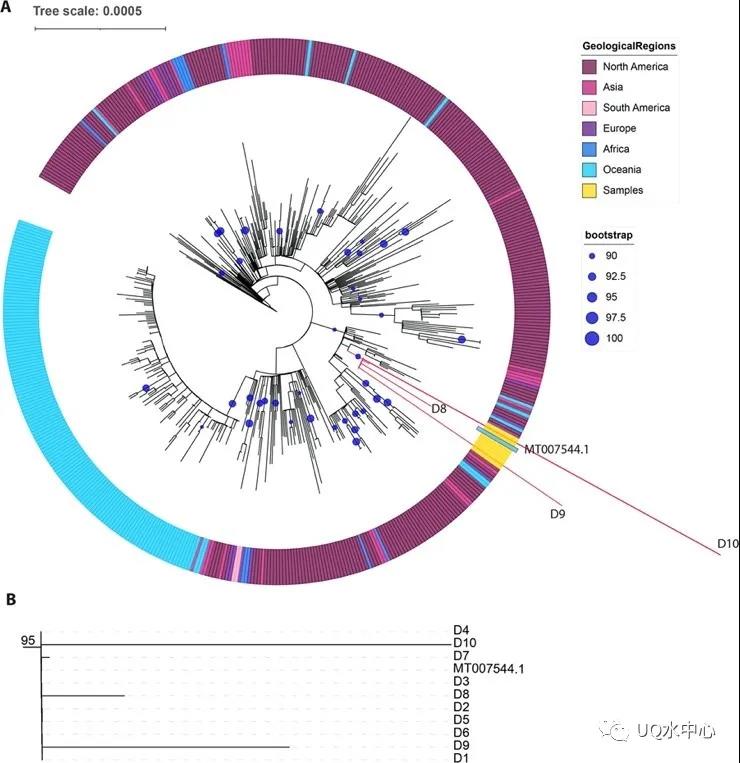
图3.阳性样本系统发育分析
城市污水中的颗粒物中可能藏有大量病毒
以往大多数的WEB都是根据污水中的液相部分进行提取和检测,忽略了污水中固相悬浮物中吸附的病毒颗粒。使用RT-qPCR和ATOPlex技术对RNA提取物进行分析的结果表明,固相中的病毒信号强度甚至高于液相部分(图4)。城市污水中的颗粒或固态物质可能藏有大量的病毒,在WEB分析中不可忽视。
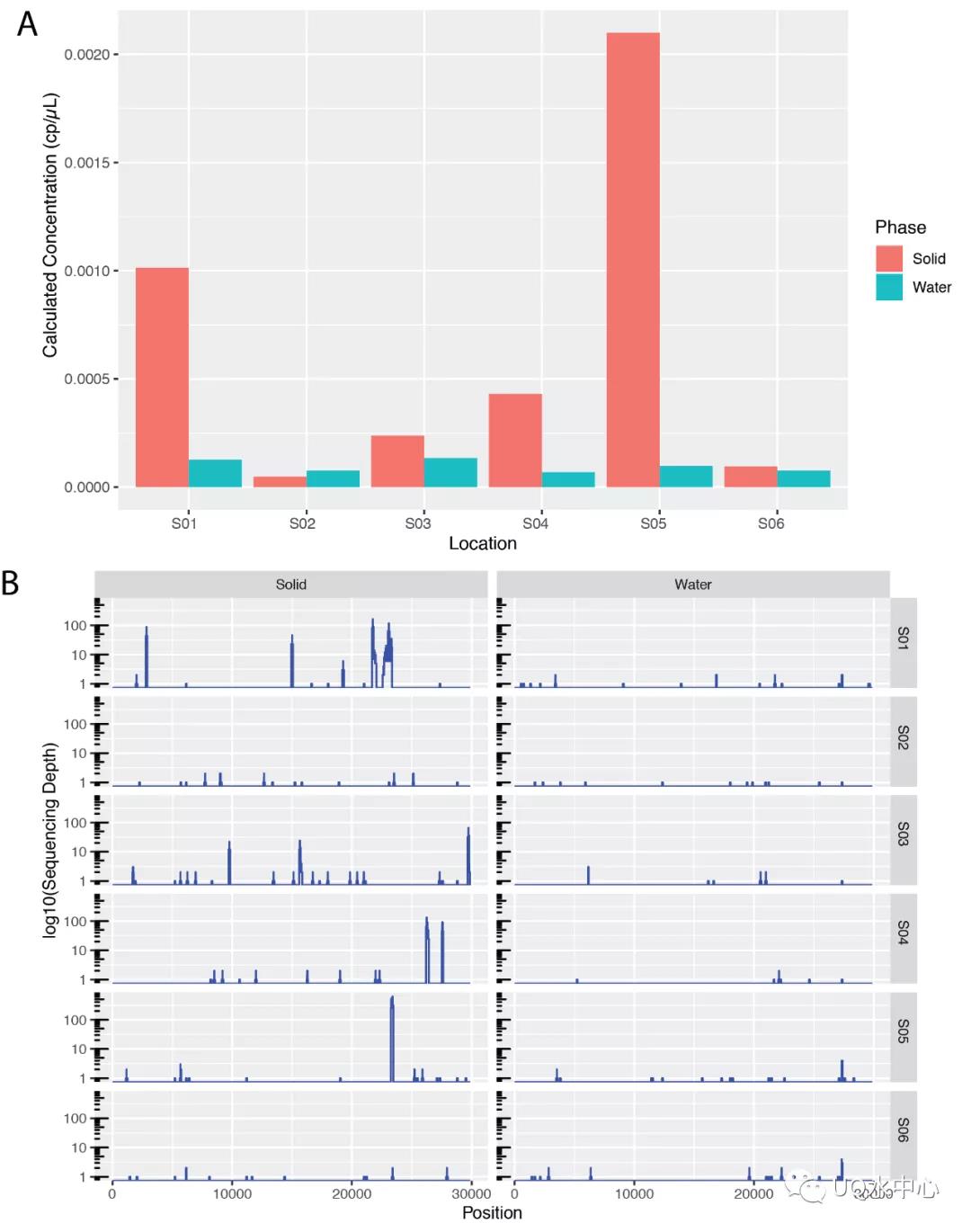
图4.污水中病毒含量固相高于液相.A:六个真实污水样品液相和固相病毒浓度对比。B:样品基因组覆盖率
总结
该研究成功将基于多重扩增子测序的新方法(即ATOPlex 技术平台)成功应用于检测城市污水中的SARS-CoV-2。该方法能实现对污水中SARS-CoV-2的高度敏及高通量定量分析,并可溯源病毒系统发育信息,从而有利于WBE 在公共卫生应急方面的进一步应用和发展。
同时,这项技术每个样本所使用的引物、PCR条件,以及生物信息分析手段都向社会公开(OpenSource),以促进技术的应用和推广。我们也期待与有兴趣的同行和机构进一步交流和合作,基于ATOPlex技术平台开发其他病原微生物的检测和溯源方案。
编译:王雨,博士研究生,昆士兰大学
第一作者:倪高风,博士后研究员,昆士兰大学
通讯作者:郭建华,副教授,昆士兰大学
昆士兰大学AWMC团队成员:卢际,Nova Maulani,王志尧,袁志国,胡氏虎
华大团队成员:田巍、杨林、杨碧澄、Ivon Harliwong
昆士兰大学QAEHS成员:Jochen Mueller
原文链接
Ni, G., Lu, J., Maulani, N., Tian, W., Yang, L., Harliwong,I., Wang, Z., Mueller, J., Yang, B., Yuan, Z., Hu, S., & Guo, J. (2021). Novel Multiplexed Amplicon-Based Sequencing to Quantify SARS-CoV-2 RNA from Wastewater. Environmental Science & Technology Letters. https://doi.org/10.1021/acs.estlett.1c00408
昆士兰大学水管理高等研究中心昆士兰大学水管理高等研究中心(Advanced Water Management Centre,AWMC,http://www.awmc.uq.edu.au) 成立于1996年,是目前国际公认的顶尖水处理技术创新中心之一。
中心位于昆士兰大学圣卢西亚校区,拥有800平方米的办公及实验面积和1000多万澳元的仪器设备, 主要致力于利用微生物学、过程工程学、化学及数学等手段进行污水处理、水回收利用及废物资源化的基础和应用研究工作。水管理高等研究中心主要包括水-健康-环境关系,城市综合水管理,智能城市水系统,下水道管网腐蚀与臭味控制,新一代污水处理技术开发,农业资源回收,环境生物技术开发,环境-能源-碳网络,甲烷的生物转化等九大研究领域。
华大智造ATOPlex平台
ATOPlex多重PCR定制化平台是华大智造自主研发的以超高重PCR技术为核心的产品定制平台。该平台涵盖了DNA、RNA和DNA甲基化方向,可提供科研、医药、司法、农业、DTC等相关领域的个性化基因检测产品定制。
该平台涵盖了DNA、RNA和DNA甲基化方向,可提供科研、医药、司法、农业、DTC等相关领域的个性化基因检测产品定制。

 基因测序仪业务
基因测序仪业务








 技术解读
技术解读 热门应用
热门应用 组学研究(科研方向)
组学研究(科研方向) 组学研究(临床方向)
组学研究(临床方向) 文档下载
文档下载 已发表文章
已发表文章 用户成功案例
用户成功案例 在线数据集
在线数据集 多功能中心
多功能中心 客户中心
客户中心 在线支持
在线支持